Bead-basierte Multiplex-Immunoassay-Technologie
Aimplex Biosciences Inc. ist unser Partner für kundenspezifische und premixed bead-basierte Multiplex-Immunoassay-Technologie. Die Panels sind zur Verwendung mit Standard-Durchflusszytometern entwickelt, sodass kein teures Spezialequipment erforderlich ist. Derzeit werden ca. 400 Immunoassays in dem sich schnell entwickelnden Produktportfolio angeboten.
Wie funktioniert die AimPlex Multiplex-Immunoassay-Technologie?
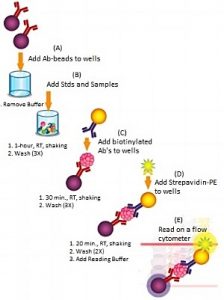
- Inkubationsschritt mit Antigen und Capture-Antikörper-konjugierten Bead (60 min.)
- Inkubationsschritt mit biotinyliertem Nachweis (30 min.)
- Streptavidin-PE-Inkubationsschritt (20 min.)
Die AimPlex Multiplex-Immunoassay-Technologie macht sich verschiedene Populationen von Beads zunutze. Sie lassen sich nach Größe und Fluoreszenzintensität aufteilen. In der Größe gibt es zwei Abstufungen; 4 und 5 Mikron (4S und 5S). Es gibt insgesamt 12 Fluoreszenzintensitätstufen. Daraus ergibt sich, dass die Technologie von AimPlex Biosciences bis zu 24 Analyte simultan detektieren kann. Das geschieht in einer einzigen Reaktion mit einer Probe von nur 15µl.
Mit Hilfe eines Standard-Durchflusszytometers werden die Bead-Populationen anschließend bestimmt. Dazu nötig ist ein Laser mit entweder blauen 488-nm- und einem roten 635-nm oder aber nur ein 488-nm-Laser. Die maximale Emission des Beadklassifizierungsfarbstoffs liegt bei 700 nm.
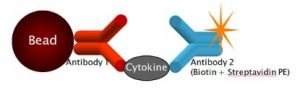
Das Verfahren an sich ähnelt dem Sandwich-ELISA Verfahren. An jede Population von Beads ist ein spezifischer Antikörper konjugiert, der das gewünschte Protein in der Probe wie ein Zytokin einfängt. Die Menge des eingefangenen Analyten wird über einen biotinylierten Antikörper gegen ein sekundäres Epitop des Proteins nachgewiesen, gefolgt von einer Streptavidin-R-Phycoerythrin-Behandlung. Auf einem herkömmlichen Durchflusszytometer wird anschließend die Fluoreszenzintensität von R-Phycoerythrin auf dem Bead gemessen. Rückschlüsse auf die Proteinkonzentration in der Probe können dann ganz einfach anhand eines Vergleiches mit der Standardkurve der Fluoreszenzsignale geschlossen werden. Letztere gewinnt man durch eine Reihenverdünnung einer bekannten Konzentration des zu untersuchenden Proteins.
Auf einen Blick: Vorteile der bead-basierten Multiplex-Immunoassay-Technologie
- 2 Bead-Größen (4S und 5S)
- 12 Fluoritätsintensitätslevel für jede Bead-Größe
- Anwendbar mit herkömmlichen Durchflusszytometern (blauer oder roter und blauer Laser)
- Klassisches Sandwich Immunoassay-Format mit Capture (cAb) und Detection (dAb) Antikörpern
- „Mix-and-Match“-Option
- Erhältlich in 32 und 96 Test-Kits
- Geringe Probengröße (15µl)
- Schneller (>2h) und kostengünstiger Immunoassay
Single-Plex Kit Bestandteile
- Analyt-Kit: analytenspezifische Ab-konjugierte Beads, Nachweisantikörper und entsprechende Antigenstandards
- Basic Kit: speziesspezifisches Nachweisantikörper-Verdünnungsmittel, Reading Buffer, Waschpuffer, Streptavidin-PE (SAPE), Filterplatte und Plattenversiegelungen
- Diluent Kit (Probenmatrix-spezifisches Verdünnungskit): probentypspezifisches Standardverdünnungsmittel und einen Probentestpuffer
Vorgemischte Multiplex-Kits
Jedes vorgemischte Multiplex-Kit verfügt über ein vordefiniertes M ultiplex-Panel mit vorgemischten Antikörper-konjugierten Beads, Antigenen und Nachweisantikörpern. Mit Ausnahme des Reading Buffers (10x) und des Waschpuffers (10x) werden alle Reagenzien gebrauchsfertig geliefert. Die meisten vorgemischten Multiplex-Kits sind in den Testgrößen 96 und 32 erhältlich.
Mix-and-Match Option
Alle verfügbaren Immunoassays sind in 12 bis 24 Analyte pro Gruppe eingeteilt. Jeder Analyt in einer Gruppe hat eine einzigartige Beadsregion. Analyte derselben Gruppe können in jeder Kombination problemlos nach den individuellen Forschungsfragen zusammengestellt werden. Analyte in verschiedenen Gruppen können zusammengestellt werden, können jedoch eine gewisse Kreuzreaktivität aufweisen. Für Fragen diesbezüglich stehen wir Ihnen jederzeit zur Verfügung.
